# 确认TOP/BOT链和A/B等位基因的基本规则
由于DNA链的定义和方向会随着数据库或者参考基因组版本的不同(比如NCBI基因版本更新)而不同,这就为确定SNP的DNA链和碱基信息造成了挑战。为解决这个问题,Illumina定义了基于序列内容的方式来定义DNA链方向的top/bottom (TOP/BOT)链和A/B等位基因命名规则,这种命名规则得以不用考虑所参考的数据库和基因组版本。
**1: 明确的SNPs, 例如 \[A/ (G or C)] 或者 \[T/ (G or C)]**
对于非 \[A/T] 或\[G/C]的SNPs:A永远定义成在Top链上,T永远定义成在Bottom链上。A和T碱基定义成“A等位基因”,G和C碱基定义成“B等位基因”。
**2: 不明确的 SNPs, 例如 \[A/T] or \[G/C]**
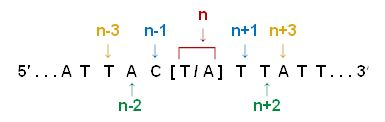
针对\[A/T]或者\[G/C]的SNPs:使用序列往5’端及3’端 移步的方式确定TOP/BOT链,然后定义A/B等位基因。
2.1 使用序列往5’端及3’端移步的方法来指定链:
1)首先, 把SNP的位置定义为 “n” 。位置n的上游5'端和下游3’端各1个的碱基位置则为 “n-1” 和 “n+1” 。n上游5’端和下游3’端各2个的碱基位置则为 “n-2” 和 “n+2” 。以此类推。
2)检测 “n-1” | “n+1” ,是否是一个明确的SNPs组合对?即其中一个是A或T另外一个是G或C。
a. 如果不是,继续检测n-2|n+2。如果有必要的话,继续往前5’端往后3’端序列移步的方法直到找到一个n-x|n+x对,即其中一个是A或T另外一个是G或C。然后继续步骤 2.1 2) b。
b. 如果是的话,那么 “A”或“T”是在不明确SNP位置(“n”)的5’端还是 3’端?
如果是5’端,该链是TOP链。
如果是3’端,该链是BOT链。
2.2. 定义核酸名称为A等位基因或B等位基因
针对TOP链:如果是\[A/T]类的SNPs,A等位基因=“A”,B等位基因=“T”。 如果是\[G/C] 类的SNPs,A等位基因 = “C” ,B等位基因 = “G”。
针对BOT链:如果是\[A/T]类的SNPs,A等位基因=“T”,B等位基因=“A”。 如果是\[G/C] 类的SNPs,A等位基因 = “G” ,B等位基因 = “C”。
更多信息,请参考技术文档[“TOP/BOT” Strand and “A/B” Allele](https://www.illumina.com/documents/products/technotes/technote_topbot.pdf)
\
\
\
| |
| :---------------------------------------------------------------------------------------------------------------------------------------------------------------------------------------------------------------------------------------------------------------------------------------------------------------------------------------------------------------: |
| *For any feedback or questions regarding this article (Illumina Knowledge Article #7135), contact Illumina Technical Support* [*techsupport@illumina.com*](mailto:techsupport@illumina.com?subject=Question%2FFeedback%20Regarding%20Illumina%20Knowledge%20Article%20#000007135%20-%20Microarray%20\&body=Dear%20Illumina%20Technical%20Support,%0D%0A%0D%0A)*.* |
---
# Agent Instructions: Querying This Documentation
If you need additional information that is not directly available in this page, you can query the documentation dynamically by asking a question.
Perform an HTTP GET request on the current page URL with the `ask` query parameter:
```
GET https://knowledge.illumina.com/microarray/general/microarray-general-reference_material-list/000007135.md?ask=
```
The question should be specific, self-contained, and written in natural language.
The response will contain a direct answer to the question and relevant excerpts and sources from the documentation.
Use this mechanism when the answer is not explicitly present in the current page, you need clarification or additional context, or you want to retrieve related documentation sections.